DEPDC1B - Википедия - DEPDC1B
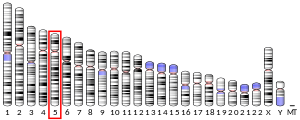
Домен DEP, содержащий белок 1B также известный как XTP1, XTP8, XAg-трансактивированный белок HBV 8, [ранее называлось BRCC3 ] человек белок закодировано ген с похожим названием, расположенный на хромосома 5.[5][6][7]
Точная функция DEPDC1B в настоящее время неизвестна. Профили экспрессии показывают, что DEPDC1B высоко экспрессируется повсеместно в тканях человека.[8]
Структура гена
Джин соседство
DEPDC1B находится на длинном плече хромосомы 5 (5q12.1), охватывая 103kb на минусовой цепи. Окрестности гена DEPDC1B включают 5 других генов. Ниже по течению идут два гена СЕНТЯБРЬ 21 и PDE4D. Вверх по течению - еще два гена ELOV7 и КРТ8П31. На нити комплемента находится другой ген в том же регионе. ЧАСТЬ 1.[6]
Промоутер
Промоторная область DEPDC1B содержит несколько факторов транскрипции, связанных с белками повсеместной экспрессии. Эти факторы транскрипции являются центральной темой клеточной пролиферации, регуляции клеточного цикла, апоптоза и дифференцировки. В этом регионе также существует несколько промоторов, уникальных для подавления опухоли или опухолевого генеза.[9]
Ниже приводится список 20 основных прогнозируемых факторов транскрипции:
|
|
|
|
структура мРНК
Варианты сращивания

DEPDC1B содержит 13 вариантов сплайсинга мРНК, которые образуют две изоформы. Изоформа 1 - самая длинная и наиболее часто используемая версия гена. Он состоит из 11 экзонов и имеет длину 103254 п.н. Изоформа 2 является вторым подтвержденным вариантом транскрипта. Он состоит из 10 экзонов, в которых отсутствует десятый экзон первого варианта. Отсутствующий экзон имеет длину 186 п.н.[10] Видеть Структура белка раздел для более подробной информации ...
Вторичная структура
Предполагается, что DEPDC1B будет преимущественно альфа-спиральным. С белком не существует значимых бета-цепей или бета-структур.[11]
Стволовые петли и связывание миРНК
Предполагается, что DEPDC1B будет обладать несколькими стержневые петли в его 5 'и 3' нетранслируемых областях (UTR)[12][13]. В 3 'UTR miRNA имеет-miR-499-5p связывается с нуклеотидной областью, предсказанной как петля ствола.[14]
Белковая структура
Последовательность
Ген DEPDC1B содержит две новые протеоформы. Наиболее часто используется самый длинный вариант, кодируемый изоформой 1 мРНК. Длина белка составляет 529 аминокислот. Вторая новая протеоформа, DEPDC1B.2, кодируется 10 экзонами, в которых отсутствует 10-й экзон самого длинного варианта. Длина белка составляет 467 аминокислот. Недостающие 62 аминокислоты следуют за доменом RhoGAP в области, которая, по прогнозам, сильно фосфорилирована.[15]
Домены

DEPDC1B содержит два структурных домена: Домен DEP и RhoGAP домен.
Домен DEP в основном находится в белках, участвующих в G-белок сигнальные пути и регулирование GTPase.[16][17] Кроме того, экспериментальные данные свидетельствуют о том, что домен DEP определяет субклеточную мишень некоторых белков, активирующих GTPase.[18] В белке DEPDC1B электронный вывод подтвердил функцию активности активатора GTPase.[15] Структура раствора человека, содержащего белки, содержащие домен DEP, подтверждает вторичную структуру домена: содержащий три альфа-спирали и две бета-цепи в пределах примерно 80 аминокислотной области домена.[19][20]
Домен RhoGAP - это еще один структурный домен, который, как известно, взаимодействует с GTPase и малой GTPase. Исследования, касающиеся домена в других белках, указывают на примерно схожую функцию домена в различных белках. Было подтверждено, что домен взаимодействует с другими белками с образованием комплексов или взаимодействует с другими структурами клетки, такими как цитоскелет или же плазматическая мембрана.[21]
Посттрансляционная модификация
Предполагается, что белковый продукт DEPDC1B будет сильно фосфорилирован после трансляции.[22] Единственный сайт сумоилирования, обнаруженный в домене RhoGAP, указывает на возможное взаимодействие белка с SUMO белок, разрешая или запрещая взаимодействие с другими белками.[23] Единственный сайт пальмитоилирования, обнаруженный в домене RhoGAP, указывает на возможное взаимодействие белкового продукта DEPDC1B с мембраной через липидный якорь.[24]
В составе зрелого белкового продукта DEPDC1B не прогнозируется никаких консервативных сайтов гликоляции.[25] Нет сигнального пептида или трансмембранные домены предсказываются в человеческом или любом ортологическом белке.[26][27] Сайты пренилирования не предсказываются ни для каких ортологов DEPDC1B.[28]
Выражение

Сообщается, что экспрессия DEPDC1B в значительной степени повсеместна в тканях мышей. Высокий уровень экспрессии генов наблюдается во все периоды жизни, кроме ранних стадий зиготы.[8] Экспериментальные данные подтверждают, что DEPDC1B проявляет сходную повсеместную экспрессию во всех тканях.[29]
Профили дифференциальной экспрессии предполагают, что DEPDC1B более выражен при многих злокачественных заболеваниях, включая: папиллярный рак щитовидной железы,[30] рак молочной железы,[31] синовиальная саркома,[32] и прогрессирование рака простаты.[33] Кроме того, экспрессия DEPDC1B снижается в условиях истощения бета-катенина в линиях множественных миеломных клеток.[34]
Взаимодействия
Никаких взаимодействий DEPDC1B с любым другим белковым продуктом, охарактеризованным экспериментально, не подтверждено.[35]
Средняя коэкспрессия DEPDC1B с ECT2 в регуляции клеточного цикла и синтезе ДНК было подтверждено сходством экспрессии в различных тканях.[35] Оставшееся предсказанное взаимодействие было определено с помощью сбора данных.
Гомология
Ортологи
DEPDC1B уникален для Хордовые в королевстве Animalia[36]
Множественное выравнивание последовательностей подтверждает, что DEPDC1B высоко консервативен среди ортологов.[37][38][39][40]Два структурных домена (DEP и RhoGAP) являются двумя наиболее консервативными элементами белков. Различные мотивы также сохраняются по всему белку. Не удалось определить данные, предполагающие функцию мотива. Все предсказано посттрансляционная модификация подтвердили, что они консервативны в ортологичных белках.
Прогнозируется, что эволюция DEPDC1B будет следовать общей эволюции видов.
| Род и виды | Распространенное имя | Учебный класс | Дивергенция (миа)[41] | Присоединение | Процент идентичности[36] |
|---|---|---|---|---|---|
| Nomascus leucogenys | Северный белощёкий гиббон | Млекопитающие | 20.4 | XP_003266016 [1] | 98% |
| Папио анубис | Оливковый павиан | Млекопитающие | 29 | XP_003899752 [2] | 98% |
| Mus musculus | Домовая мышь | Млекопитающие | 92.3 | NP_848798 [3] | 94% |
| Pteropus alecto | Черная летучая лисица | Млекопитающие | 94.2 | XP_006906108 [4] | 96% |
| Felis catus | Домашняя кошка | Млекопитающие | 94.2 | XP_003981045 [5] | 96% |
| Bos taurus | Корова | Млекопитающие | 94.2 | XP_005221558 [6] | 95% |
| Monodelphis domestica | Серый короткохвостый опоссум | Млекопитающие | 162.6 | XP_001363879 [7] | 88% |
| Ficedula albicollis | Ошейниковая мухоловка | Пр. | 296 | XP_005060715 [8] | 77% |
| Taeniopygia guttata | Зебра зяблик | Пр. | 296 | XP_002188294 [9] | 76% |
| Gallus gallus | Курица | Пр. | 296 | NP_001006576 [10] | 75% |
| Анолис каролинский | Зеленый анол | Рептилии | 296 | XP_003216290 [11] | 76% |
| Xenopus tropicalis | Западная когтистая лягушка | Амфибия | 371.2 | NP_001121488 [12] | 68% |
| Lepisosteus oculatus | Пятнистый гар | Актиноптеригии | 400.1 | XP_006626875 [13] | 68% |
| Зебра Майландия | Зебра мбуна | Актиноптеригии | 400.1 | XP_004566850 [14] | 57% |
Паралоги

DEPDC1B обладает двумя важными паралогами - DEPDC1A и DEPDC7
Множественное выравнивание последовательностей и филогенетический анализ указывают на DEPDC1A как на самый последний паралог, разошедшийся примерно 600 миллионов лет назад. DEPDC1A исследовали при нескольких болезненных состояниях. Высокая экспрессия белка в плазматических клетках злокачественных опухолей множественной миеломы (ММ) связана с летальным исходом. Высокая экспрессия была подтверждена с использованием условной доставки лентивирусного вектора «для ингибирования роста клеточных линий меланомы человека (HMCL) с блокировкой в фазе G2 клеточного цикла, фосфорилированием и стабилизацией p53 и накоплением p21Cip1» 9.[42] В том же исследовании был сделан вывод, что DEPDC1A может вносить вклад в свойства плазмобластов клеток MM, блокируя дифференцировку. Изучение DEPDC1A в канцерогенезе мочевого пузыря выявило этот ген как возможный антиген для образования клеток рака мочевого пузыря. Использование микроматрицы и Нозерн-блоттинга подтвердили присутствие незначительного количества белка в нормальных тканях, за исключением семенников. В настоящее время ген является потенциальной молекулой-мишенью для терапевтического лечения канцерогенеза мочевого пузыря.[43]
Никаких данных, подробно описывающих важные функции в DEPD7, не публиковалось и не регистрировалось.
Рекомендации
- ^ а б c ГРЧ38: Ансамбль выпуск 89: ENSG00000035499 - Ансамбль, Май 2017
- ^ а б c GRCm38: выпуск Ensembl 89: ENSMUSG00000021697 - Ансамбль, Май 2017
- ^ "Справочник человека по PubMed:". Национальный центр биотехнологической информации, Национальная медицинская библиотека США.
- ^ "Ссылка на Mouse PubMed:". Национальный центр биотехнологической информации, Национальная медицинская библиотека США.
- ^ Моримото, К. (1996). «Характеристика уникального варианта вируса бешенства летучих мышей, ответственного за новые случаи заболевания людей в Северной Америке». Труды Национальной академии наук. 93 (11): 5653–5658. Дои:10.1073 / пнас.93.11.5653. ЧВК 39303. PMID 8643632.
- ^ а б Энтрез Ген: DEPDC1B https://www.ncbi.nlm.nih.gov/gene?LinkName=protein_gene&from_uid=223633999
- ^ Генные карты: DEPDC1B https://www.genecards.org/cgi-bin/carddisp.pl?gene=DEPDC1B
- ^ а б NCBI GEO https://www.ncbi.nlm.nih.gov/geoprofiles
- ^ Программное обеспечение Genomatix. «Геноматикс Эльдорадо». Проверено 1998-2014.
- ^ NCBI AceView https://www.ncbi.nlm.nih.gov/IEB/Research/Acembly/av.cgi?db=human&q=DEPDC1B
- ^ BPS: AW Burgess, PK Ponnuswamy и HA Sheraga, Анализ конформаций аминокислотных остатков и прогноз топографии остова в белках, Israel J. Chem., P239-286, 1974, vol12.D_R: G. Dele`age and B. Ру, Алгоритм предсказания вторичной структуры на основе предсказания класса, Protein Engineering, p289-294, 1987, vol 1, num 4. DSC: Росс Д. Кинг и Майкл Дж. Стернберг - Идентификация и применение концепций, важных для точной и надежной предсказание вторичной структуры белков. Белковая наука, 1996, 5: 2298-2310GGR: Garnier, Gibrat, and Robson, Meth. Enzymol., R.F. Дулиттл изд. 1996, 266: 97-120GOR: Жан Гарнье, Д. Дж. Осгуторп и Барри Робсон, Анализ точности и значение простых методов для предсказания вторичной структуры белков, J. Mol. Biol., P 97-120, 1978, vol 120. G_G: O. Gascuel и JL Golmard, Простой метод предсказания вторичной структуры глобулярных белков: значение и точность, CABIOS, p 357-365, 1988, vol 4. H_K: Л. Ховард Холли и Мартин Карплюс, Предсказание вторичной структуры белка с помощью нейронной сети, Proc. Natl. Акад. Sci. USA, p 152-156, Jan 1989, vol 86. K_S: Росс Д. Кинг и Майкл Дж. Стернберг, Подход машинного обучения для предсказания вторичной структуры белка, J. Mol. Biol., P 441-457, 1990, vol 216.L_G: Джонатан М. Левин и Жан Гарнье, Улучшения в методе предсказания вторичной структуры, основанном на поиске локальных гомологий последовательностей и его использовании в качестве инструмента построения модели, Biochim. Биофиз. Acta., P 283-295, 1988, vol 955. Q_S: Нин Цянь и Теренс Сейновски, Предсказание вторичной структуры белков с использованием моделей нейронных сетей, J. Mol. Biol., P 865-884, 1988, vol 202.JOI Совместное предсказание - Прогноз, сделанный программой, которая назначает структуру с использованием процедуры «победитель получает все» для каждого предсказания аминокислот с использованием других методов.
- ^ Mfold http://mfold.rna.albany.edu/
- ^ Sfold http://sfold.wadsworth.org/
- ^ TragetScan http://www.targetscan.org/
- ^ а б Q8WUY9 (DEP1B_HUMAN) https://www.uniprot.org/uniprot/Q8WUY9
- ^ Burchett SA (октябрь 2000 г.). «Регуляторы передачи сигналов G-белка: бестиарий модульных белковых связывающих доменов». Журнал нейрохимии. 75 (4): 1335–51. Дои:10.1046 / j.1471-4159.2000.0751335.x. PMID 10987813. S2CID 37038615.
- ^ Вонг ХК, Мао Дж., Нгуен Дж. Т., Сринивас С., Чжан В., Лю Б., Ли Л., Ву Д., Чжэн Дж. (Декабрь 2000 г.). «Структурная основа распознавания растрепанного домена DEP в сигнальном пути Wnt». Структурная биология природы. 7 (12): 1178–84. Дои:10.1038/82047. ЧВК 4381838. PMID 11101902.
- ^ Мартемьянов, К; и другие. (2003). «Домен DEP определяет субклеточное нацеливание белка, активирующего GTPase RGS9, in vivo». Журнал неврологии. 23 (12): 10175–10181. Дои:10.1523 / JNEUROSCI.23-32-10175.2003. ЧВК 6741003. PMID 14614075.
- ^ Zhang HP, Hayashi F, Yokoyama S. (2007) Структура раствора домена dep из белка 1, содержащего домен dep человека. https://www.ncbi.nlm.nih.gov/Structure/mmdb/mmdbsrv.cgi?uid=2ysr
- ^ Мадей Т., Аддесс К.Дж., Фонг Дж. Х., Гир Л. Я., Гир Р. К., Ланчицкий С. Дж., Лю С., Лу С., Марчлер-Бауэр А., Панченко А. Р., Чен Дж., Тиссен П. А., Ван И, Чжан Д., Брайант Ш. «MMDB: трехмерные структуры и макромолекулярные взаимодействия». Исследования нуклеиновых кислот. 40 (Выпуск базы данных): D461–4. Дои:10.1093 / нар / gkr1162. ЧВК 3245041. PMID 22135289.
- ^ Пек Дж., Дуглас Дж., Ву СН, Бурбело П.Д. (сентябрь 2002 г.). «Белки, содержащие домен RhoGAP человека: структура, функция и эволюционные отношения». Письма FEBS. 528 (1–3): 27–34. Дои:10.1016 / s0014-5793 (02) 03331-8. PMID 12297274. S2CID 30443852.
- ^ Блом Н., Гаммельтофт С., Брунак С. (декабрь 1999 г.). «Последовательность и предсказание на основе структуры сайтов фосфорилирования эукариотических белков». Журнал молекулярной биологии. 294 (5): 1351–62. Дои:10.1006 / jmbi.1999.3310. PMID 10600390.
- ^ Expasy SumoSP http://sumosp.biocuckoo.org/
- ^ Expasy CSS-Palm http://csspalm.biocuckoo.org/
- ^ Прогнозирование сайтов N-гликозилирования в белках человека. Р. Гупта, Э. Юнг и С. Брунак. В стадии подготовки, 2004 г.
- ^ Cserzö M, Eisenhaber F, Eisenhaber B, Simon I (2002). «О фильтрации ложноположительных предсказаний трансмембранного белка». Белковая инженерия. 15 (9): 745–52. Дои:10.1093 / белок / 15.9.745. PMID 12456873.
- ^ Петерсен Т.Н., Брунак С., фон Хейне Г., Нильсен Н. (2011). «SignalP 4.0: отличия сигнальных пептидов от трансмембранных областей». Nat. Методы. 8 (10): 785–6. Дои:10.1038 / nmeth.1701. PMID 21959131. S2CID 16509924.
- ^ Expasy PrePS http://mendel.imp.ac.at/sat/PrePS/index.html
- ^ BioGPS http://biogps.org/#goto=genereport&id=55789
- ^ NCBI GEO https://www.ncbi.nlm.nih.gov/geoprofiles/18885436
- ^ NCBI GEO https://www.ncbi.nlm.nih.gov/geoprofiles/36185472M
- ^ NCBI GEO https://www.ncbi.nlm.nih.gov/geoprofiles/38187695
- ^ NCBI GEO https://www.ncbi.nlm.nih.gov/geoprofiles/14261636
- ^ NCBI GEO https://www.ncbi.nlm.nih.gov/geoprofiles/61462636
- ^ а б Нить http://string-db.org/newstring_cgi/show_network_section.pl
- ^ а б NCBI BLAST http://blast.ncbi.nlm.nih.gov/Blast.cgi
- ^ Хиггинс Д.Г., Близби А.Дж., Фукс Р. (апрель 1992 г.). «CLUSTAL V: улучшенное программное обеспечение для множественного выравнивания последовательностей». Компьютерные приложения в биологических науках. 8 (2): 189–91. Дои:10.1093 / биоинформатика / 8.2.189. PMID 1591615.
- ^ Томпсон Дж. Д., Хиггинс Д. Г., Гибсон Т. Дж. (Ноябрь 1994 г.). «CLUSTAL W: повышение чувствительности прогрессивного множественного выравнивания последовательностей за счет взвешивания последовательностей, штрафов за пропуски в зависимости от позиции и выбора весовой матрицы». Исследования нуклеиновых кислот. 22 (22): 4673–80. Дои:10.1093 / nar / 22.22.4673. ЧВК 308517. PMID 7984417.
- ^ Фельзенштейн, J (1989). «PHYLIP - Пакет вывода филогении (версия 3.2)». Кладистика. 5: 164–166. Дои:10.1111 / j.1096-0031.1989.tb00562.x. S2CID 221547732.
- ^ CLUSTAL W: Джули Д. Томпсон, Десмонд Г. Хиггинс и Тоби Дж. Гибсон, модифицированные; любые ошибки связаны с модификациями. ФИЛИП: Фельзенштейн, Дж. 1993. PHYLIP (пакет вывода филогении), версия 3.5c. Распространяется автором. Департамент генетики Вашингтонского университета, Сиэтл.
- ^ Хеджес С.Б., Дадли Дж., Кумар С. (декабрь 2006 г.). «TimeTree: общедоступная база знаний о временах расхождения между организмами». Биоинформатика. 22 (23): 2971–2. Дои:10.1093 / биоинформатика / btl505. PMID 17021158.
- ^ Кассамбара А, Шонхалс М., Моро Дж., Вейрун Дж. Л., Рем Т., Гольдшмидт Х, Шланг D, Кляйн Б. (2013). «Ингибирование DEPDC1A, плохого прогностического маркера множественной миеломы, задерживает рост и индуцирует маркеры зрелых плазматических клеток в злокачественных плазматических клетках». PLOS ONE. 8 (4): e62752. Дои:10.1371 / journal.pone.0062752. ЧВК 3640027. PMID 23646139.
- ^ Канехира М., Харада Ю., Таката Р., Шуин Т., Мики Т., Фуджиока Т., Накамура Ю., Катагири Т. (сентябрь 2007 г.). «Участие позитивной регуляции DEPDC1 (домен DEP, содержащий 1) в канцерогенезе мочевого пузыря». Онкоген. 26 (44): 6448–55. Дои:10.1038 / sj.onc.1210466. PMID 17452976.